Single Nucleotide Polymorphism (SNP)
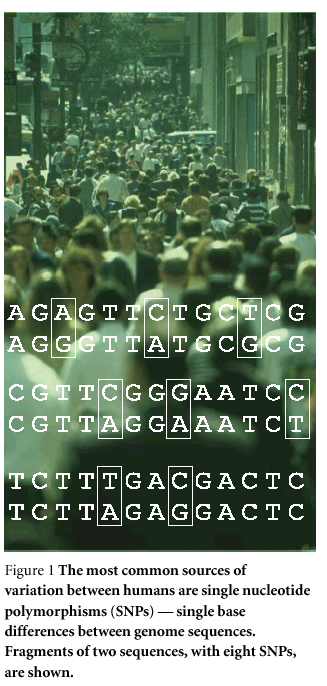
- Le polymorphisme le plus commun chez l'homme.
- Stable
- Beaucoup n'ont pas d'implications fonctionnelles
- 1 SNP tous les 100 à 300 nt. 3 200 000 dans le génome.
- En comparant 2 individus, on trouve un SNP toutes les 1000/2000 bases.
Applications
- Les SNP constituent une trace historique pour l'étude de la phylogénie humaine:
ils mutent lentement et ont peu de chance de réapparaitre de façon récurente.
- Les SNP sont à l'origine de susceptibilité ou de resistance à de nombreuses
maladies.
- Cartographie de maladies à caractères complexes (cancers, diabète,
maladies mentales)
- Prédiction des réponses aux drogues.
- Haplotypes: combinaison d'allèles tendant
à être transmis ensemble. On estime que la recherche d'haplotype à l'échelle du
génome pour l'ensemble des maladies requiert une cartographie très dense
avec jusqu'à 1 million de marqueurs. Les SNP répondent à ce critère. Ils sont donc
utilisés non seulement comme éléments "mutateurs", mais comme marqueurs permettant d'en
découvrir d'autres.
Types de SNP
Les SNP peuvent être classées selon qu'elles sont
- codantes/non codantes
- Codant affectant l'aa/sans affecter l'aa
- Affectant l'aa avec modification de propriétés / sans modification
- Région régulatrice/autre région non codante
- 14500 SNP tombrent dans des exons de refseq (environ 2 par gène)
Deux stratégies d'obtention de SNP
- Fragments de restriction de 2 génomes différents + séquençage des fragments
homologues + clustering et comparaison informatique.
- Nouvelles séquences shotgun + alignement sur le génomique.
-
Autres polymorphismes:
- Insertions, délétions, duplications, réarrangements
- Plus rares et moins bien compris
Extrait de l'article sur le génome humain (à comprendre):
In addition to sequencing large-insert clones, three [sequencing] centres
generated a large collection of random raw sequence reads from whole-genome
shotgun libraries. These 5.77 million successful sequences contained
2.4 Gb of high-quality bases; this corresponds to about 0.75-fold coverage and
would be statistically expected to include about 50% of the nucleotides in the
human genome (data available at http://snp.cshl.org/data).
