Cartographie Génétique (Cartes de liaison)
La fréquence de crossing over entre 2
marqueurs
indique la distance qui les sépare. Les marqueurs doivent
être
polymorphes pour être suivis.
Les marqueurs moléculaires (phénotype
visible
sur gel) ont fait nettement progresser cette technique.
RFLP (restriction fragment length polymorphism)
-
Des fragments d'ADN génomiques qui, hybridés à un
ADN génomique digéré par une enzyme de
restriction,
donnent des bandes de taille différente selon les individus.
-
Les marqueurs sont assignés aux chromosomes par FISH
(Fluorescent
in situ hybridization). Résolution: sous-bande chromosomique
(env.
10 Mb)
Microsatellites
-
Des séquences répétées avec fort taux de
polymorphisme:
le nombre de répétitions varie fortement d'un individu
à
l'autre.
-
Une PCR suffit pour identifier quel allèle est présent
chez
un individu: deux amorces autour du microsatellite, amplification puis
résolution sur gel. On observe soit deux bandes pour les
allèles maternel et paternel, soit une seule bande si même
allèle.
STS (Sequence tagged Sites)
- Séquence génomique unique de 200-500bp
pouvant être amplifiée à partir d'amorces PCR
connues.
Hybrides d'irradiation
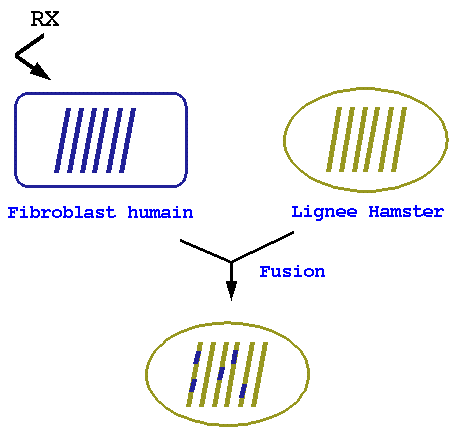
- On recherche ensuite ce que deviennent des marqueurs: retrouver
2
marqueurs dans le même hybride indique leur proximité. Par
exemple, utilisation des marqueurs STS: le marqueur STS s1 est
retrouvé dans les hybrides hi,hj,hk, le marqueur s2 est
retrouvé dans les hybrides hl, hm, etc. De ces données,
on déduit une proximité ou non des marqueurs s1 et
s2.
- Résolution: 1-2Mb
Carte généthon de 1996
-
5264 microsatellites, résolution 1,6 cM (~3 Mb)

